ডিএনএ অনুলিপন
আণবিক জীববিজ্ঞানে, ডিএনএ অনুলিপন বা ডিএনএ প্রতিলিপন (ইংরেজি: DNA replication) হলো একটি জৈবিক প্রক্রিয়া যার মাধ্যমে একটি ডিএনএ অণু থেকে একই রকম দুটি ডিএনএ-এর প্রতিলিপি উৎপন্ন হয়।[১] ডিএনএ প্রতিলিপি জৈবিক উত্তরাধিকারের জন্য সবচেয়ে প্রয়োজনীয় অংশ হিসেবে কাজ করে। কোষ বিভাজনের সময় ক্ষতিগ্রস্ত টিস্যুর বৃদ্ধি এবং মেরামতের জন্য এটি অত্যন্ত প্রয়োজনীয়, যখন এটি নিশ্চিত করে যে নতুন কোষের প্রতিটি নিজস্ব ডিএনএ অনুলিপি গ্রহণ করে।[২] কোষ বিভাজনের স্বতন্ত্র বৈশিষ্ট্য যা ডিএনএ অনুলিপন অপরিহার্য করে তোলে।
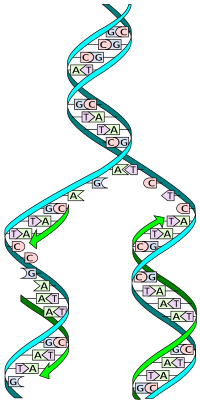
ডিএনএ দুটি পরিপূরক স্ট্র্যান্ড বা সূত্রকের একটি দ্বি-সূত্রক দিয়ে তৈরি। দ্বি-সূত্রক বলতে একটি দ্বি-সূত্রী ডিএনএর উপস্থিতির বর্ণনা দেয় যা দুটি সরলরৈখিক সূত্রকের সমন্বয়ে গঠিত ও একে অপরের বিপরীতে চলে এবং একসাথে প্যাঁচানো থাকে।[৩] প্রতিলিপনের সময় এই সূত্রকগুলো পৃথক হয়ে যায়। মূল ডিএনএ অণুর প্রতিটি সূত্রক তার পরিপূরক সূত্রক উৎপাদনের জন্য টেমপ্লেট হিসাবে কাজ করে, এই প্রক্রিয়াটিকে অর্ধ-সংরক্ষণমূলক প্রতিলিপন হিসেবে চিহ্নিত করা হয়। অর্ধ-রক্ষণশীল প্রতিলিপনের ফলস্বরূপ, নতুন সূত্র একটি মূল ডিএনএ সূত্রকের পাশাপাশি একটি নতুন সংশ্লেষিত সূত্রকের সমন্বয়ে গঠিত হয়।[৪] কোষীয় প্রুফ রিডিং এবং ত্রুটি-চেক করার পদ্ধতিগুলো ডিএনএ প্রতিলিপনের বিশ্বস্ততা নিশ্চিত করে।[৫][৬]
একটি কোষে, ডিএনএ অনুলিপন নির্দিষ্ট অবস্থান জিনোমে[৭] শুরু হয় যাতে একটি প্রাণীর জিনগত উপাদান রয়েছে।[৮] নতুন সূত্রকের উৎপত্তির সময় হেলিকেজ নামক এনজাইম ডিএনএ-এর প্যাঁচ খুলতে সাহায্য করে যাতে দুটি রেপ্লিকেশন ফর্ক তৈরি হয়। ডিএনএ সংশ্লেষণের সূচনা এবং ধারাবাহিকতায় সহায়তার জন্য অনেকগুলো প্রোটিন প্রতিলিপি রেপ্লিকেশন ফর্কের সাথে যুক্ত থাকে। প্রধানত ডিএনএ পলিমারেজ এনজাইম নিউক্লিওটাইড যুক্ত করে নতুন সূত্রক সংশ্লেষ করে যা প্রতিটি (টেমপ্লেট) সূত্রকের পরিপূরক। ইন্টারফেজের এস- পর্যায়ে ডিএনএ প্রতিলিপন ঘটে থাকে।
ডিএনএ প্রতিলিপন (ডিএনএ বিবর্ধন) গবেষণাগারেও (কৃত্রিমভাবে, একটি কোষের বাইরে) করা যেতে পারে। কোষ থেকে বিচ্ছিন্ন ডিএনএ পলিমারেজ এবং কৃত্রিম ডিএনএ প্রাইমারগুলো একটি টেমপ্লেট ডিএনএ অণুতে ডিএনএ সংশ্লেষণ শুরু করতে ব্যবহার করা যেতে পারে। পলিমারেজ চেইন বিক্রিয়া (পিসিআর), লাইগেজ চেইন বিক্রিয়া (এলসিআর), এবং ট্রান্সক্রিপশন প্রভাবিত পরিবর্ধন (টিএমএ) এর উদাহরণ।
সংঘটন স্থান সম্পাদনা
ইউক্যারিওটিক কোষের ইন্টারফেজ দশার নিউক্লিয়াসে এবং প্রোক্যারিওটিক কোষের সাইটোপ্লাজমে ডিএনএ প্রতিলিপিকরণ হয়ে থাকে।
ডিএনএর গঠন সম্পাদনা
ডিএনএ একটি ডাবল হেলিক্স স্ট্রাকচার নিয়ে গঠিত, উভয় স্ট্র্যান্ড বা সূত্রক একত্রে কুন্ডলিত হয়ে চারিত্রিক বৈশিষ্ট্যযুক্ত ডাবল হেলিক্স গঠন করে। ডিএনএর প্রতিটি সূত্রক হল চার ধরনের নিউক্লিওটাইডের একটি শৃঙ্খল। ডিএনএর নিউক্লিওটাইডগুলোতে একটি ডিঅক্সিরাইবোজ চিনি, একটি ফসফেট এবং নিউক্লিওবেস থাকে। চার ধরনের নিউক্লিওটাইড চার ধরনের নিউক্লিওবেস এর সাথে সম্পৃক্ত যেমন - এডেনিন, সাইটোসিন, গুয়ানিন, এবং থাইমিন যাদের সংক্ষিপ্ত রূপ হল A, C, G এবং T। এডেনিন এবং গুয়ানিন হল পিউরিন বেস, যেখানে সাইটোসিন এবং থাইমিন হল পাইরিমিডিন বেস। এই নিউক্লিওটাইড সমূহ ফসফো-ডাইএস্টার বন্ধন গঠন করে, যার মাধ্যমে ডিএনএ ডাবল হেলিক্সের ফসফেট-ডিঅক্সিরাইবোজ ব্যাকবোন তৈরি করে যার নিউক্লিওবেসগুলো অভ্যন্তরের দিকে নির্দেশ করে (যেমন, বিরোধী সূত্রকের দিকে)। নিউক্লিওবেসগুলো সুত্রকের মধ্যে হাইড্রোজেন বন্ড দ্বারা যুক্ত হয়। এডেনিন থাইমিনের সাথে (দুটি হাইড্রোজেন বন্ধন) এবং গুয়ানিন সাইটোসিনের সাথে (তিনটি হাইড্রোজেন বন্ধন) দ্বারা যুক্ত হয়।
ডিএনএ সূত্রকের একটি দিকনির্দেশ আছে এবং একক সূত্রকের দুটি ভিন্ন প্রান্তকে 3 ′ (তিন-পূরক) প্রান্ত এবং 5 ′ (পাঁচ-পূরক) প্রান্ত বলা হয়। প্রচলিত নিয়ম অনুসারে, যদি ডিএনএর একক স্ট্র্যান্ডের বেস সিকোয়েন্সটি দেওয়া থাকে তবে সিকোয়েন্সের বাম প্রান্তটি 5 ′ প্রান্ত হয় এবং ক্রমের ডান প্রান্তটি 3 ′ প্রান্ত হয়। ডাবল হেলিক্সের সূত্রক দুটি বিপরীত ও সমান্তরাল যেমন একটি 5 ′ থেকে 3 ′ এবং বিপরীত সূত্রক 3 ′ থেকে 5 ′। এই পদগুলো দ্বারা ডিঅক্সিরাইবোজ এর যে কার্বন পরমাণুতে শৃঙ্খলের পরবর্তী ফসফেট সংযুক্ত থাকে তা নির্দেশ করে। ডিএনএ সংশ্লেষণে দিকনির্দেশ প্রভাব আছে, কারণ ডিএনএ পলিমারেজ একটি ডিএনএ সূত্রকের 3 ′ প্রান্তে নিউক্লিওটাইড যুক্ত করে কেবল এক দিকে ডিএনএ সংশ্লেষ করতে পারে।
ডিএনএতে পরিপূরক বেসগুলোর সংযোজন (হাইড্রোজেন বন্ধনের মাধ্যমে) এর অর্থ প্রতিটি স্ট্র্যান্ডের মধ্যে থাকা তথ্যগুলো অপ্রয়োজনীয়। ফসফো-ডাইএস্টার (অন্তঃ-স্ট্র্যান্ড) বন্ডগুলো হাইড্রোজেন (আন্তঃ-স্ট্র্যান্ড) বন্ডের চেয়ে শক্তিশালী। ফসফো-ডাইএস্টার বন্ডগুলোর আসল কাজ হল ডিএনএ পলিমারগুলোতে একটি নিউক্লিওটাইডের 5 ' কার্বনকে অন্য নিউক্লিওটাইডের 3' কার্বনের সাথে সংযুক্ত করা, অন্যদিকে হাইড্রোজেন বন্ডগুলো হেলিক্স ১-অক্ষের বাইরে ডিএনএ ডাবল হেলিক্স কে স্থির করে তবে অক্ষের দিকে নয়।[৯] এটি স্ট্র্যান্ডগুলোকে একে অপরের থেকে পৃথক হতে দেয়। একক স্ট্র্যান্ডের নিউক্লিওটাইডগুলো তাই নতুন সংশ্লেষিত অংশীদার স্ট্র্যান্ডের নিউক্লিওটাইডগুলোকে পুনর্গঠন করতে ব্যবহার করে।[১০]
ডিএনএ পলিমারেজ সম্পাদনা
ডিএনএ পলিমারেজগুলো এনজাইমের একটি পরিবার যা সমস্ত ধরনের ডিএনএ প্রতিলিপন ঘটিয়ে থাকে।[১১] সাধারণভাবে ডিএনএ পলিমেরেসগুলো নতুন স্ট্র্যান্ডগুলোর সংশ্লেষণ শুরু করতে পারে না, তবে কেবলমাত্র একটি বিদ্যমান ডিএনএ বা আরএনএ স্ট্র্যান্ডকে ছাঁচ স্ট্র্যান্ডের সাথে যুক্ত করে প্রসারিত করতে পারে। সংশ্লেষণ শুরু করতে আরএনএ-এর একটি সংক্ষিপ্ত টুকরো যাকে একটি প্রাইমার বলা হয়, এটি তৈরি করতে হয় এবং টেমপ্লেট ডিএনএ স্ট্র্যান্ডের সাথে যুক্ত করতে হয়।
ডিএনএ পলিমারেজ ফসফো-ডাইএস্টার বন্ধন একটি বিদ্যমান নিউক্লিওটাইড চেইনের প্রান্তকে প্রসারিত করে ডিএনএর একটি নতুন স্ট্র্যান্ড তৈরি করে এবং একই সময়ে টেমপ্লেট স্ট্র্যান্ডের সাথে মিলিত করে নতুন নিউক্লিওটাইড যুক্ত করে। ডিএনএ পলিমারকরণের এই প্রক্রিয়াটির জন্য প্রয়োজনীয় শক্তি প্রতিটি মুক্ত ক্ষারের সাথে সংযুক্ত তিনটি ফসফেটের মধ্যে উচ্চ-শক্তি সম্পন্ন ফসফেট (ফসফোনহাইড্রাইড) বন্ধনের আর্দ্র বিশ্লেষণ থেকে আসে। মুক্ত ক্ষারগুলোকে তাদের সংযুক্ত ফসফেট গ্রুপগুলোর সাথে নিউক্লিওটাইড বলে, বিশেষত তিনটি ফসফেট সংযুক্ত বেসগুলোকে নিউক্লিওসাইড ট্রাইফসফেট বলা হয়। যখন একটি নিউক্লিওটাইড ক্রমবর্ধমান ডিএনএতে যোগ হয়, তখন ক্রমবর্ধমান চেইন নিউক্লিওটাইড নিকটবর্তী ফসফেট মধ্যে একটি ফসফো-ডাইএস্টার বন্ধন গঠন করার জন্য প্রয়োজনীয় শক্তি একটি উচ্চ শক্তি সম্পন্ন ফসফেট বন্ধন আর্দ্র বিশ্লেষণের দ্বারা পাইরোফসফেট হিসেবে প্রকাশিত হয়। পাইরোফসফেটের এনজাইমেটিক হাইড্রোলাইসিসের ফলস্বরূপ অজৈব ফসফেট দ্বিতীয় উচ্চ-শক্তি সম্পন্ন ফসফেট বন্ধন গ্রহণ করে এবং বিক্রিয়াটিকে কার্যকরভাবে একমুখী করে তোলে।
সাধারণভাবে ডিএনএ পলিমারেজগুলো অত্যন্ত নির্ভুল, প্রতি ১০৭ নিউক্লিওটাইড যুক্ত করার জন্য একটির চেয়ে কম অভ্যন্তরীণ ত্রুটির হার যুক্ত হয়।[১২] এছাড়াও কিছু ডিএনএ পলিমারেজেরর প্রুফ রিডিং ক্ষমতাও রয়েছে; ভুল ক্ষারগুলোকে সংশোধন করার জন্য তারা ক্রমবর্ধমান স্ট্র্যান্ডের প্রান্ত থেকে নিউক্লিওটাইডগুলো সরিয়ে ফেলতে পারে। অবশেষে অনুলিপন-পরবর্তী মেরামত প্রক্রিয়া ত্রুটি নির্ণয়ের জন্য ডিএনএ পর্যবেক্ষণ করে, মূল স্ট্র্যান্ড ক্রম থেকে নতুন সংশ্লেষিত ডিএনএ স্ট্র্যান্ডের সাথে অমিলগুলো পৃথক করতে সক্ষম হয়। একইসাথে এই তিনটি বৈষম্য নির্ণয় পদক্ষেপ প্রতি ১০৯ নিউক্লিওটাইড যুক্ত করার জন্য একটিরও কম ভুলের প্রতিলিপন করতে সক্ষম করে।[১২]
একটি জীবন্ত কোষে ডিএনএ প্রতিলিপনের হার সর্বপ্রথম ফাজ সংক্রমিত E. coli-তে T4 ফাজ (ভাইরাস) ডিএনএ প্রসারিত হওয়ার হার হিসেবে পরিমাপ করা হয়েছিল।[১৩] ৩৭ ডিগ্রি সেলসিয়াস ডিএনএ বৃদ্ধি পাওয়ার সময়কালে এই হার প্রতি সেকেন্ডে ৭৪৯ নিউক্লিওটাইড ছিল। T4 ফাজ ডিএনএ সংশ্লেষণের সময় প্রতি জোড়া ক্ষার পরিবর্তনের হার প্রতি ১০৮ নিউক্লিওটাইডে ছিল ১.৭।[১৪]
প্রতিলিপন প্রক্রিয়া সম্পাদনা
সমস্ত জৈবিক পলিমারকরণ প্রক্রিয়াগুলোর মতো ডিএনএ প্রতিলিপন তিনটি অনুঘটিত এবং সমন্বিত পদক্ষেপে সম্পন্ন হয়: আরম্ভ, দীর্ঘায়ন এবং সমাপ্তি।
আরম্ভ সম্পাদনা
কোষ বিভাজনের করার জন্য প্রথমে এটির ডিএনএর প্রতিলিপি অবশ্যই তৈরি করতে হয়।[১৫] ডিএনএর প্রতিলিপন একবার শুরু হয়ে গেলে এটি সমাপ্তির দিকে এগিয়ে যায়। প্রতিলিপি সম্পূর্ণ হয়ে গেলে একই কোষ চক্রে এটি আবার সংঘটিত হয় না। প্রাক-রেপ্লিকেশন কমপ্লেক্সের আরম্ভের বিভাজনের দ্বারা এটি সম্ভব হয়।
প্রাক-রেপ্লিকেশন কমপ্লেক্স সম্পাদনা
মাইটোসিসের শেষের দিকে এবং G1 পর্বের প্রথম দিকে, প্রারম্ভিক প্রোটিনগুলোর একটি বৃহৎ অংশ ডিএনএর নির্দিষ্ট পয়েন্ট এ প্রাক-রেপ্লিকেশন কমপ্লেক্স একত্রিত হয়, যা "উৎস" হিসেবে পরিচিত।[৭] E. coli তে প্রাথমিক প্রোটিন হল DnaA; ইস্ট এর জন্য জন্য একটি উৎস শনাক্তকারী কমপ্লেক্স।[১৬] প্রবর্তক প্রোটিন দ্বারা ব্যবহৃত সিকোয়েন্সগুলো এডেনিন ও থাইমিন ক্ষারগুলোতে সমৃদ্ধ হয়ে থাকে, কারণ ক্ষার জোড়গুলোতে দুটি হাইড্রোজেন বন্ধন থাকে (সাইটোসিন-গুয়ানিন জোড়ায় বন্ধন থাকে) এবং তাই একে সহজেই প্রসারিত করে আলাদা করা যায়।[১৭] প্রকৃত কোষের জীবে উৎস শনাক্তকারী কমপ্লেক্স প্রারম্ভিক প্রোটিনকে প্রাক-রেপ্লিকেশন কমপ্লেক্সে রূপান্তরে প্রভাবিত করে। তারপরে Cdc6 এবং Cdt1 ডিএনএর আবদ্ধ উৎস শনাক্তকারী কমপ্লেক্স সাথে যুক্ত হয়ে Mcm কমপ্লেক্সটি লোড করার জন্য প্রয়োজনীয় কমপ্লেক্স গঠন করে। Mcm কমপ্লেক্স হলো হেলিকেজ যা প্রকৃতকোষীতে প্রতিলিপন উৎস এবং প্রতিলিপন ফর্ক গঠন করে। Mcm কমপ্লেক্সটি G1 পর্বের শেষ ভাগে গঠিত হয় এবং ORC-Cdc6-Cdt1 কমপ্লেক্সটি ATP-নির্ভর প্রোটিন পুনরায় তৈরির মাধ্যমে ডিএনএতে লোড হয়। মূল ডিএনএতে Mcm কমপ্লেক্সের লোডিং প্রাক-রেপ্লিকেশন কমপ্লেক্স গঠনের সমাপ্তি চিহ্নিত করে।[১৮]
G1 দশার শেষের দিকে পরিবেশগত অবস্থা ঠিক থাকলে, যেমন G1 এবং G1/S cyclin - Cdk কমপ্লেক্স সক্রিয় হয়, যা জিনের অভিব্যক্তিকে উদ্দীপিত করে যা ডিএনএ সিন্থেটিক বড় যন্ত্র গঠন করে। এছাড়াও G1/S-Cdk অ্যাক্টিভেশন S-Cdk কমপ্লেক্সগুলোর প্রকাশ এবং সক্রিয় হতে উদ্দীপিত করে, যা প্রজাতি এবং কোষ ভেদে প্রতিলিপনের উৎস সক্রিয় করতে ভূমিকা রাখে। এই Cdk এর নিয়ন্ত্রণ কোষের ধরন এবং বিকাশের পর্যায়ের উপর নির্ভর করে পরিবর্তিত হয়। এই নিয়ন্ত্রণটি মুকুলোদগমকারী ইস্টে ভালোভাবে বোঝা যায়, যেখানে S সাইক্লিনস Clb5 এবং Clb6 মূলত ডিএনএ প্রতিলিপনের জন্য দায়ী।[১৯] Clb5,6-Cdk1 কমপ্লেক্সগুলো প্রতিলিপন উৎসের সক্রিয়করণকে সরাসরি ট্রিগার করে এবং তাই প্রতিটি উৎসকে সরাসরি সক্রিয় করতে এস পর্যায়ে জুড়ে এটি প্রয়োজন।[১৮]
অনুরূপণ পদ্ধতিতে প্রতিলিপন উৎস সক্রিয় করতে এস দশার মধ্যে Cdc7ও প্রয়োজনীয়। Cdc7 পুরো চক্র জুড়ে সক্রিয় থাকে না এবং ডিএনএ প্রতিলিপনের অপ্রাপ্ত আরম্ভ এড়ানোর জন্য এটির সক্রিয়করণ কঠোরভাবে প্রয়োজন হয়। G1 এর শেষের দিকে নিয়ন্ত্রক উপ-একক Dbf4 এর সাথে সংঘর্ষের ফলে Cdc7-এর ক্রিয়াকলাপ হঠাৎ বেড়ে যায় যা Cdc7-কে সরাসরি বেঁধে রাখে এবং এর প্রোটিন কাইনেজ ক্রিয়াকলাপ প্রচার করে। Cdc7টি মূল ক্রিয়াকলাপের হার-সীমাবদ্ধ নিয়ামক হিসাবে প্রমাণিত হয়েছে। একইসাথে G1/S-Cdks অথবা S-Cdks এবং Cdc7 সরাসরি প্রতিলিপন মূলককে সক্রিয় করতে সহযোগিতা করে, যার ফলে ডিএনএ সংশ্লেষণের সূচনা হয়।[১৮]
প্রাক-প্রারম্ভিক কমপ্লেক্স সম্পাদনা
প্রারম্ভিক এস পর্যায়ে S-Cdk এবং Cdk7 অ্যাক্টিভেশন প্রাক-প্রারম্ভিক কমপ্লেক্সের সমাবেশের দিকে পরিচালিত করে, একটি বৃহৎ প্রোটিন যৌগ গঠিত হয়। প্রাক-প্রারম্ভিক কমপ্লেক্সের গঠনটি Cdc6 এবং Cdt1-কে মূল রেপ্লিকেশন কমপ্লেক্স থেকে বিচ্ছিন্ন করে, প্রাক-রেপ্লিকেশন কমপ্লেক্সকে নিষ্ক্রিয় করে এবং ছত্রভঙ্গ করে। প্রাক-প্রারম্ভিক কমপ্লেক্সটি উৎসের উপর লোড হলে Mcm হেলিকেজকে সক্রিয় করে, যার ফলে ডিএনএ সূত্রকে মুক্ত হয়। প্রাক-প্রারম্ভিক কমপ্লেক্সটি ডিএনএ-তে আলফা-প্রাইমেজ এবং অন্যান্য ডিএনএ পলিমারেজগুলো লোড করে।[১৮]
আলফা-প্রাইমেজ নামে প্রথম প্রাইমার সংশ্লেষিত করবার পর প্রাইমার-ছাঁচ জংশনগুলো ক্ল্যাম্প লোডারের সাথে ক্রিয়া করে, যা ডিএনএ সংশ্লেষণ শুরু করতে স্লাইডিং ক্ল্যাম্পটি ডিএনএ-এর উপর চাপিয়ে দেয়। প্রাক-প্রারম্ভিক কমপ্লেক্সের উপাদানগুলো মূল থেকে বেরিয়ে যাওয়ার সাথে সাথে প্রতিলিপন ফর্কের সাথে যুক্ত হয়।[১৮]
দীর্ঘায়ন সম্পাদনা
ডিএনএ পলিমারেজে 5′–3′ কার্যকলাপ রয়েছে। সমস্ত প্রচলিত ডিএনএ প্রতিলিপি সিস্টেমে সংশ্লেষণ শুরুর আগে একটি মুক্ত 3′ হাইড্রোক্সিল গ্রুপ প্রয়োজন (দ্রষ্টব্য: ডিএনএ টেমপ্লেটটি 3′ থেকে 5′ দিকে পড়া হয় যেখানে একটি নতুন স্ট্র্যান্ড 5′ থেকে 3′ দিকের দিকে সংশ্লেষিত হয়; এটি প্রায়শই বিভ্রান্তকর হয়)। ডিএনএ সংশ্লেষণের জন্য চারটি স্বতন্ত্র প্রক্রিয়া স্বীকৃত আছে-
- সমস্ত কোষীয় জীব এবং অনেকগুলো ডিএনএ ভাইরাস, ফাজ এবং প্লাজমিড প্রাইমেজ ব্যবহার করে একটি মুক্ত 3′ হাইড্রোক্সিল গ্রুপের সাথে একটি সংক্ষিপ্ত আরএনএ প্রাইমার সংশ্লেষিত করে যা পরবর্তীকালে ডিএনএ পলিমারেজ দ্বারা প্রসারিত হয়।
- রেট্রো উপাদানগুলো (রেট্রোভাইরাসসহ) একটি ট্রান্সফার আরএনএ নিয়োগ করে রিভার্স ট্রান্সক্রিপটেজ দ্বারা প্রসারিত করার জন্য ডিএনএর প্রতিলিপনকে একটি মুক্ত 3′ হাইড্রোক্সিল গ্রুপ সরবরাহ করে।
- এডিনোভাইরাস এবং ফাই 29 পরিবারের ব্যাকটেরিওফাজের এর মধ্যে 3′ হাইড্রোক্সিল গ্রুপ জিনোম সংযুক্ত প্রোটিন এর অ্যামিনো অ্যাসিড পার্শ্ব-শৃঙ্খল (টার্মিনাল প্রোটিন) থেকে সরবরাহ করা হয় যা নিউক্লিওটাইডের ডিএনএ পলিমারেজ দ্বারা যুক্ত হয়ে একটি নতুন সূত্রক গঠন করে।
- একসূত্র বিশিষ্ট ডিএনএ ভাইরাস (একটি গ্রুপ রয়েছে যেখানে আছে circoviruses, geminiviruses, parvoviruses এবং অন্যান্য) এবং অনেক ফাজ ও প্লাসমিড যে ঘূর্ণায়মান বৃত্ত রেপ্লিকেশন (RCR) প্রক্রিয়া ব্যবহার করেন, RCR এন্ডোনিউক্লিয়েজ একটি জিনোম স্ট্র্যান্ড সৃষ্টি করে (একক স্ট্র্যান্ড ভাইরাস) বা ডিএনএ স্ট্র্যান্ড সৃষ্টি করে (প্লাজমিড)। নিকড স্ট্র্যান্ডের 5′ প্রান্তটি নিউক্লিয়েজের একটি টাইরোসিন অবশিষ্টাংশে স্থানান্তরিত হয় এবং মুক্ত 3′ হাইড্রোক্সিল গ্রুপটি ডিএনএ পলিমারেজ দ্বারা নতুন স্ট্র্যান্ড সংশ্লেষ করার জন্য ব্যবহৃত হয়।
প্রথমটি এই ব্যবস্থাগুলোর মধ্যে সর্বাধিক পরিচিত এবং কোষীয় জীব দ্বারা ব্যবহৃত হয়। এই ব্যবস্থায় একবার দুটি স্ট্র্যান্ড পৃথক হয়ে গেলে প্রাইমেজ টেমপ্লেট স্ট্র্যান্ডগুলোতে আরএনএ প্রাইমার যুক্ত করে। লিডিং স্ট্র্যান্ড একটি আরএনএ প্রাইমার গ্রহণ করে যখন ল্যাগিং স্ট্র্যান্ড বেশ কয়েকটি গ্রহণ করে। লিডিং স্ট্র্যান্ড ক্রমাগত অবিচ্ছিন্নভাবে একটি ডিএনএ পলিমেরেজ দ্বারা প্রাইমার থেকে প্রসারিত হয়েছে, যখন ল্যাগিং স্ট্র্যান্ড প্রতিটি প্রাইমার থেকে বিরচন করে বিচ্ছিন্নভাবে ওকাজাকি টুকরায় পরিণত হয়। আরএনএনেজ আরএনএ প্রাইমার খণ্ডগুলোকে সরিয়ে দেয় এবং শূন্যস্থান পূরণের জন্য প্রতিরক্ষামূলক পলিমারেজ থেকে স্বল্প প্রক্রিয়াকরণ ডিএনএ পলিমারেজ প্রবেশ করে। এটি সম্পূর্ণ হয়ে গেলে লিডিং স্ট্র্যান্ডের একটি একক নিক এবং ল্যাগিং স্ট্র্যান্ডের বেশ কয়েকটি নিক পাওয়া যায়। লাইগেজ এই নিকগুলো পূরণ করার জন্য কাজ করে, এইভাবে নতুন করা ডিএনএ অণু প্রতিলিপি সম্পূর্ণ হয়।
এই প্রক্রিয়ায় ব্যবহৃত প্রাইমেজে ব্যাকটেরিয়া এবং আর্চিয়া/ইউক্যারিওটের মধ্যে উল্লেখযোগ্যভাবে পার্থক্য রয়েছে। ব্যাকটেরিয়া DnaG প্রোটিনের সাথে সম্পর্কিত একটি প্রাইমেজ ব্যবহার করে যা সুপার-ফ্যামিলি TOPRIM ভাঁজ টাইপের একটি অনুঘটক ডোমেইন ধারণ করে।[২০] TOPRIM ভাঁজটিতে রসম্যান-জাতীয় টপোলজিতে চারটি সংরক্ষিত স্ট্র্যান্ডসহ একটি আলফা/বিটা কোর রয়েছে। এই কাঠামোটি টপোইসোমারেজ I, টপোইসোমারেজ II, ওল্ড-ফ্যামিলি নিউক্লিয়েজ এবং RecR প্রোটিন সম্পর্কিত ডিএনএ মেরামতকারী প্রোটিনগুলোর অনুঘটক ডোমেনগুলোও পাওয়া যায়।
বিপরীতে আর্চিয়া এবং ইউক্যারিওট দ্বারা ব্যবহৃত প্রাইমেজে আরএনএ রিকগনিশন মোটিফ (RPM) এর একটি সংস্করণ রয়েছে। এই প্রাইমেজ কাঠামোগতভাবে অনেক ভাইরাস সম্পর্কিত আরএনএ নির্ভর আরএনএ পলিমারেজ, রিভার্স ট্রান্সক্রিপটেজ, চক্রীয় নিউক্লিওটাইড উৎপাদনকারী চক্র এবং ডিএনএ প্রতিলিপি এবং মেরামতের সাথে জড়িত এ/ বি/ওয়াই পরিবারের ডিএনএ পলিমারেযের মতো। ইউক্যারিওটিক প্রতিলিপনে প্রাইমেজ পোল-আলফার সাথে একটি কমপ্লেক্স গঠন করে।[২১]
একাধিক ডিএনএ পলিমারেজ ডিএনএ প্রতিলিপন প্রক্রিয়ায় বিভিন্ন ভূমিকা গ্রহণ করে। E. coli, DNA Pol III হলো পলিমারেজ এনজাইম যা ডিএনএ রেপ্লিকেশন এর জন্য প্রাথমিকভাবে দায়ী। এটি সম্পূর্ণ প্রতিরূপ চক্রের জন্য অক্ষত থেকে, অত্যন্ত উচ্চ উৎপাদন প্রদর্শন করে এমন প্রতিলিপন ফর্কের সাথে একটি রেপ্লিকেশন কমপ্লেক্সে একত্রিত হয়। বিপরীতে DNA Pol I হলো আরএনএ প্রাইমারগুলো ডিএনএর সাথে প্রতিস্থাপনের জন্য দায়ী এনজাইম। DNA Pol I-এর পলিমারেজ ক্রিয়াকলাপ ছাড়াও একটি 5′ থেকে 3′ এক্সোনিউক্লিয়েজ কার্যকলাপ রয়েছে এবং এটি আরএনএ প্রাইমারকে এর পিছনে ডিএনএ স্ট্র্যান্ডকে প্রসারিত করার জন্য এর এক্সোনিউক্লিয়েজ ক্রিয়াকলাপটি ব্যবহার করে নিক অনুবাদ বলে। পোল-১ পোল-৩ এর তুলনায় অনেক কম প্রক্রিয়াজাতক কারণ ডিএনএ প্রতিলিপনে এটির প্রাথমিক কাজ হলো কয়েকটি খুব দীর্ঘ অঞ্চলের পরিবর্তে অনেকগুলো সংক্ষিপ্ত ডিএনএ অঞ্চল তৈরি করা।
ইউক্যারিওটে কম উৎপাদনশীল এনজাইম Pol-α প্রতিলিপন কাজ সূচনা করতে সাহায্য করে কারণ এটি প্রাইমেজের সঙ্গে একটি কমপ্লেক্স গঠন করে।[২২] ইউক্যারিওটে লিডিং স্ট্র্যান্ড সংশ্লেষণ Pol-ε দ্বারা পরিচালিত হয় বলে মনে করা হয়; যাইহোক, এই দৃশ্যটি সম্প্রতি চ্যালেঞ্জ করা হয়েছে, Pol-δ-এর জন্য একটি ভূমিকা প্রস্তাব করা হয়েছে।[২৩] প্রাইমারের অপসারণ সম্পূর্ণ Pol-δ করে যেখানে Pol-ε প্রতিলিপনের সময় ডিএনএ মেরামত সম্পন্ন করে।[২৪]
ডিএনএ সংশ্লেষণ চলার সাথেসাথে মূল ডিএনএ স্ট্র্যান্ডগুলো বুদ্বুদের প্রতিটি পাশের দিকে উন্মুক্ত হয়ে দুটি কাঁটাবিশিষ্ট একটি রেপ্লিকেশন ফর্ক গঠন করে। বৃত্তাকার ক্রোমোজোমে প্রতিলিপির একটি মাত্র উৎস থাকা ব্যাকটেরিয়াতে এই প্রক্রিয়ায় একটি থিটা কাঠামো" তৈরি হয় (গ্রীক অক্ষর থিটা: θ-এর অনুরূপ)। বিপরীতে ইউক্যারিওটের দীর্ঘতর সরলরৈখিক ক্রোমোজোম থাকে এবং এর মধ্যে একাধিক উৎসে প্রতিলিপি শুরু হয়।[২৫]
রেপ্লিকেশন ফর্ক সম্পাদনা
রেপ্লিকেশন ফর্ক একটি কাঠামো যা ডিএনএ প্রতিলিপি চলাকালীন দীর্ঘ সূত্রকীয় ডিএনএর মধ্যে উৎপন্ন হয়। এটি হেলিকেজ দ্বারা তৈরি করা হয়, যা সূত্রকে দুটি ডিএনএ স্ট্র্যান্ডকে ধরে রেখে হাইড্রোজেন বন্ধনগুলো ভেঙে দেয়। ফলস্বরূপ কাঠামোতে দুটি শাখা "কাঁটা" রয়েছে, যার প্রত্যেকটিই ডিএনএর একক স্ট্র্যান্ড দ্বারা গঠিত। এই দুটি স্ট্র্যান্ড লিডিং এবং ল্যাগিং স্ট্র্যান্ডগুলোর ছাঁচ হিসাবে কাজ করে, যা ডিএনএ পলিমারেজ টেমপ্লেটগুলোর পরিপূরক নিউক্লিওটাইডগুলোর সাথে মিলে তৈরি হয়; টেমপ্লেটগুলো সঠিকভাবে লিডিং স্ট্র্যান্ড ছাঁচ এবং ল্যাগিং স্ট্র্যান্ড ছাঁচ হিসাবে উল্লেখ করা যেতে পারে।
ডিএনএ 3′ থেকে 5′ দিকে ডিএনএ পলিমারেজ দ্বারা পড়া হয়, যার অর্থ নতুন স্ট্র্যান্ড 5 'থেকে 3' দিকে সংশ্লেষিত হয়। যেহেতু লিডিং এবং ল্যাগিং স্ট্র্যান্ড ছাঁচগুলো রেপ্লিকেশন ফর্কে বিপরীতমুখী, তাই একটি বড় সমস্যা হলো নতুন ল্যাগিং স্ট্র্যান্ড ডিএনএ-এর সংশ্লেষণ কীভাবে অর্জন করা যায়, যার সংশ্লেষণের দিকটি ক্রমবর্ধমান রেপ্লিকেশন ফর্ক এর দিকের বিপরীত হবে।
লিডিং স্ট্র্যান্ড সম্পাদনা
লিডিং স্ট্র্যান্ড হলো নতুন ডিএনএর যে স্ট্র্যান্ড ক্রমবর্ধমান রেপ্লিকেশন ফর্কের একই দিকে সংশ্লেষিত। এই ধরনের ডিএনএ প্রতিলিপন অবিচ্ছিন্ন হয়।
ল্যাগিং স্ট্র্যান্ড সম্পাদনা
ল্যাগিং স্ট্র্যান্ড হলো নতুন ডিএনএ-এর সেই স্ট্র্যান্ড যার সংশ্লেষণের দিকটি ক্রমবর্ধমান রেপ্লিকেশন ফর্কের দিকের বিপরীত। এর ওরিয়েন্টেশনের কারণে লিডিং স্ট্র্যান্ডের তুলনায় ল্যাগিং স্ট্র্যান্ডের প্রতিলিপন আরও জটিল। ফলস্বরূপ, এই স্ট্র্যান্ডের ডিএনএ পলিমারেজকে অন্য স্ট্র্যান্ডের "পিছনে" থাকতে দেখা যায়।
ল্যাগিং স্ট্র্যান্ড সংক্ষিপ্ত ও পৃথক অংশে সংশ্লেষিত হয়। ল্যাগিং স্ট্র্যান্ড টেমপ্লেটে একজন প্রাইমেজ টেমপ্লেট ডিএনএ-কে "পড়ে" এবং একটি সংক্ষিপ্ত পরিপূরক আরএনএ প্রাইমারের সংশ্লেষণ শুরু করে। একটি ডিএনএ পলিমারেজ ওকাজাকি টুকরো তৈরি করে প্রাইমড অংশগুলোকে প্রসারিত করে। এরপর আরএনএ প্রাইমারগুলো ডিএনএ দ্বারা অপসারণ ও প্রতিস্থাপন করা হয় এবং ডিএনএর টুকরোগুলো ডিএনএ লাইগেজের মাধ্যমে একত্রিত হয়।
রেপ্লিকেশন ফর্কের গতিশীলতা সম্পাদনা
সমস্ত ক্ষেত্রে হেলিকেজটি ছয়টি পলিপেপটাইডের সমন্বয়ে গঠিত যা ডিএনএর প্রতিলিপনের সময় একটি স্ট্র্যান্ডের চারপাশে মোড়ানো থাকে। দুটি পলিমারেজ হেলিকেজ হেক্সিমারের সাথে আবদ্ধ থাকে। ইউক্যারিওটসে হেলিকেজটি লিডিং স্ট্র্যান্ডের চারপাশে মোড়ানো থাকে এবং প্রোক্যারিওটসে এটি ল্যাগিং স্ট্র্যান্ডের চারপাশে মোড়ানো থাকে।[২৬]
হেলিকেজ যখন রেপ্লিকেশন ফর্কে ডিএনএ-কে খুলে দেয়, ঠিক তখন ডিএনএ ঘুরতে বাধ্য হয়। এই প্রক্রিয়াটির ফলস্বরূপ ডিএনএ-তে সামনের দিকে মোড় নেয়।[২৭] এই প্রক্রিয়াটি একটি ঘূর্ণনশীল প্রতিরোধের রূপ দেয় যা শেষ পর্যন্ত রেপ্লিকেশন ফর্ক এর অগ্রগতি থামিয়ে দেয়। টপোইসোমারেজ হলো এক ধরনের এনজাইম যা অস্থায়ীভাবে ডিএনএর স্ট্র্যান্ডগুলো ভেঙে দেয়, ডিএনএ সূত্রকে দুটি স্ট্র্যান্ডকে বিচ্ছিন্ন করার ফলে সৃষ্ট উত্তেজনা থেকে মুক্তি দেয়; টপোইসোমারেজগুলো (ডিএনএ গাইরেজসহ) ডিএনএ হেলিক্সে নেতিবাচক সুপারকয়েল যুক্ত করে এটি সম্পন্ন করে।[২৮]
শূন্য একক-আটকে থাকা ডিএনএ গৌণ কাঠামো গঠনে নিজেই ফিরে যায়; এই কাঠামোগুলো ডিএনএ পলিমারেজের চলাচলে হস্তক্ষেপ করতে পারে। এটি রোধ করতে একক-স্ট্র্যান্ড বাইন্ডিং প্রোটিনগুলো ডিএনএতে আবদ্ধ থাকে যতক্ষণ পর্যন্ত না দ্বিতীয় স্ট্র্যান্ড সংশ্লেষিত না হয়, যা গৌণ কাঠামো গঠনে বাধা দেয়।[২৯]
ডাবল-স্ট্র্যান্ডেড ডিএনএ হিস্টোনগুলোর চারপাশে যুক্ত থাকে যা জিনের এক্সপ্রেশন নিয়ন্ত্রণে গুরুত্বপূর্ণ ভূমিকা পালন করে, তাই প্রতিলিপি যুক্ত ডিএনএ অবশ্যই হিস্টোনের আশেপাশে মূল ডিএনএ হিসেবে একই স্থানে যুক্ত থাকে। এটি নিশ্চিত করার জন্য হিস্টোন চ্যাপেরোনস এটি প্রতিলিপনের আগেই ক্রোমাটিন থেকে পৃথক হয় এবং হিস্টোনকে সঠিক জায়গায় প্রতিস্থাপন করে। এই পুনঃনির্মাণের কিছু পদক্ষেপ কিছুটা অনুমানমূলক।[৩০]
ক্ল্যাম্প প্রোটিনগুলো ডিএনএর চারপাশে একটি স্লাইডিং ক্ল্যাম্প গঠন করে, ডিএনএ পলিমারেজকে তার টেমপ্লেটের সাথে যোগাযোগ বজায় রাখতে সহায়তা করে, যার ফলে উৎপাদনে সহায়তা হয়। ক্ল্যাম্পের অভ্যন্তরীণ মুখ ডিএনএ-এর মাধ্যমে খাঁজ কাটতে সক্ষম করে। একবার পলিমারেজ টেমপ্লেটের শেষ প্রান্তে পৌঁছে যায় বা ডাবল-স্ট্র্যান্ডেড ডিএনএ শনাক্ত করে, যা স্লাইডিং ক্ল্যাম্প একটি ধারণামূলক পরিবর্তন করে যার ফলে ডিএনএ পলিমারেজ প্রকাশিত হয়। ক্ল্যাম্প-লোডিং প্রোটিনগুলো ক্ল্যাম্প লোড করার জন্য প্রাথমিকভাবে টেমপ্লেট এবং আরএনএ প্রাইমার এর মধ্যে জংশনকে চিহ্নিত করে।[৬]
ডিএনএ প্রতিলিপন প্রোটিন সম্পাদনা
রেপ্লিকেশন ফর্কে অনেকগুলো প্রতিলিপন এনজাইম ডিএনএ-তে একত্রিত করে একটি জটিল আণবিক যন্ত্র গঠন করে যা রিপ্লিজোম নামে পরিচিত। নিচে রিপ্লিজোমে অংশ নেওয়া প্রধান ডিএনএ প্রতিলিপন এনজাইমগুলোর একটি তালিকা দেওয়া হলো:[৩১] -
| এনজাইম | ডিএনএ প্রতিলিপনে কাজ |
|---|---|
| ডিএনএ হেলিকেজ | হেলিক্স অস্থিতিশীলকারী এনজাইম হিসেবেও পরিচিত। টপোইসোমারেজের পিছনে রেপ্লিকেশন ফর্কের ডিএনএর দুটি স্ট্র্যান্ডকে হেলিকেজ পৃথক করে। |
| ডিএনএ পলিমারেজ | ডিএনএ প্রতিলিপনের সময় নিউক্লিওটাইড স্তরগুলো ডিএনএতে 5′ থেকে 3′-এর দিকে সংযোজন করার জন্য দায়ী এনজাইম। প্রুফ রিডিং এবং ত্রুটি সংশোধনও করে। বিভিন্ন ধরনের ডিএনএ পলিমারেজ রয়েছে যার মধ্যে প্রতিটি বিভিন্ন ধরনের কোষে বিভিন্ন কার্য সম্পাদন করে। |
| ডিএনএ ক্ল্যাম্প | একটি প্রোটিন যা ডিএনএ মূল স্ট্র্যান্ড থেকে বিচ্ছিন্ন হয়ে ডিএনএ পলিমারেজকে দীর্ঘায়িত করে। |
| একক স্ট্র্যান্ড ডিএনএ-বাইন্ডিং প্রোটিন | ssDNA-তে আবদ্ধ হয় এবং ডিএনএ হেলিকেজের এটি খুলে ফেলার পরে ডিএনএ ডাবল হেলিক্সকে পুনরায় অ্যানিলিং করা থেকে বিরত রাখে, এভাবে স্ট্র্যান্ডের বিচ্ছিন্নতা বজায় রাখা এবং নতুন স্ট্র্যান্ডের সংশ্লেষণের সুবিধার্থে কাজ করে। |
| টোপোইসোমারেজ | ডিএনএ-কে সুপার-কয়েলড প্রকৃতি থেকে শিথিল করে। |
| ডিএনএ গাইরেজ | ডিএনএ হেলিকেজের সাহায্যে স্ট্র্যান্ডের চাপকে মুক্তি দেয়; এটি একটি নির্দিষ্ট ধরনের টোপোইসোমারেজ। |
| ডিএনএ লাইগেজ | অর্ধ-রক্ষণশীল স্ট্র্যান্ডগুলো পুনরায় যুক্ত করে এবং ল্যাগিং স্ট্র্যান্ডের ওকাজাকি অংশগুলো যোগ করে। |
| প্রাইমেজ | নতুন ডিএনএ স্ট্র্যান্ডের সংশ্লেষণ শুরু করতে ডিএনএ পলিমারেজ এর জন্য আরএনএ (অথবা ডিএনএ) একটি সূচনা পয়েন্ট সরবরাহ করে। |
| টেলোমিয়ারেজ | ইউক্যারিওটিক ক্রোমোজোমের প্রান্তে পুনরাবৃত্ত নিউক্লিওটাইড অনুক্রম যুক্ত করে টেলোমেরিক ডিএনএ কে লম্বা করে। এটি জীবাণু কোষ এবং স্টেম-সেলগুলোকে কোষ বিভাজনে হায়ফ্লিক সীমা এড়াতে সহায়তা করে।[৩২] |
প্রতিলিপন যন্ত্রপাতি সম্পাদনা
প্রতিলিপন যন্ত্রপাতি বা মেশিনারিগুলো ডিএনএর প্রতিলিপনে জড়িত নিয়ামকগুলো নিয়ে গঠিত এবং টেমপ্লেট ssDNA-তে উপস্থিত থাকে। প্রতিলিপন মেশিনারিগুলোর মধ্যে প্রিমোসোটারগুলো হলো প্রতিলিপন এনজাইম; ডিএনএ পলিমারেজ, ডিএনএ হেলিকেজ, ডিএনএ ক্ল্যাম্প এবং ডিএনএ টোপোইসোমারেজ এবং প্রতিলিপি প্রোটিন; যেমন একক স্ট্র্যান্ড ডিএনএ বাইন্ডিং প্রোটিন (SSB)। প্রতিলিপন মেশিনারিগুলোতে এই উপাদানগুলো সমন্বয় করে। বেশিরভাগ ব্যাকটেরিয়ার ডিএনএ প্রতিলিপনে জড়িত সমস্ত ফ্যাক্টরগুলো রেপ্লিকেশন ফর্কে অবস্থিত এবং কমপ্লেক্সগুলো ডিএনএ প্রতিলিপনে সময় রেপ্লিকেশন ফর্কে অবস্থান করে। এই প্রতিলিপন মেশিনারিগুলোকে রিপ্লিজোম বা ডিএনএ রেপ্লিকেশন সিস্টেম বলা হয় । এই পদগুলো রেপ্লিকেশন ফর্কে উপর অবস্থিত প্রোটিন জন্য জেনেরিক পদ হিসেবে বিবেচনা করা হয়। ইউক্যারিওটিক এবং কিছু ব্যাকটেরিয়া কোষে রিপ্লিজোমগুলো গঠিত হয় না।
যেহেতু রেপ্লিকেশন মেশিনারিগুলো কারখানার মতো টেমপ্লেট ডিএনএ-তে তুলনামূলকভাবে স্থানান্তরিত হয় না, তাই তাদের প্রতিলিপন কারখানা বলা হয়।[৩৩] বিকল্প চিত্রটিতে, ডিএনএ কারখানাগুলো প্রজেক্টরগুলোর মতো এবং ডিএনএগুলো সিনেম্যাটিক ফিল্ম এর মতো যেমন প্রজেক্টারে নিয়মিত প্রবাহিত হয়। প্রতিলিপন কারখানার মডেলটিতে ডিএনএ হেলিকেজের পরে লিডিং স্ট্র্যান্ড এবং ল্যাগিং স্ট্র্যান্ড উভয় টেমপ্লেট ডিএনএতে লোড হয়, হেলিকেজগুলো ডিএনএ বরাবর একে অপরের সাথে চালিত হয়। হেলিকেজগুলো প্রতিলিপন প্রক্রিয়ার অবশিষ্ট অংশগুলোর সাথে যুক্ত থাকে। পিটার মেইস্টার এবং তার সহযোগীরা সবুজ ফ্লোরোসেন্ট প্রোটিন (GFP) ট্যাগযুক্ত ডিএনএ পলিমারেজ আলফা পর্যবেক্ষণ করে মুকুলোদগম করে এমন ইস্টে সরাসরি প্রতিলিপন সাইটগুলো পর্যবেক্ষণ করেছেন। তাঁরা শনাক্ত করেছেন যে ট্যাগযুক্ত লোকির জোড়াগুলো প্রতিলিপন উৎস থেকে প্রতিসাম্যভাবে পৃথক করা হয়েছে এবং আবিষ্কার করেছেন যে জোড়গুলোর মধ্যে দূরত্ব সময়ের সাথে উল্লেখযোগ্যভাবে হ্রাস পায়।[৩৪] এই সন্ধানটি পরামর্শ দেয়, যে ডিএনএ প্রতিলিপন প্রক্রিয়াটি ডিএনএ কারখানার সাথে চলে। অর্থাৎ প্রতিলিপন কারখানার জোড়াগুলো প্রতিলিপন উৎস এবং একে অপরের সাথে যুক্ত কারখানাগুলোতে লোড হয়। এছাড়াও টেমপ্লেট ডিএনএগুলো কারখানায় চলে যায়, যা টেমপ্লেট ssDNAs এবং নতুন DNAs তে বহিষ্করণ নিয়ে আসে। মেইস্টারের সন্ধান প্রতিলিপন কারখানা মডেলের প্রথম প্রত্যক্ষ প্রমাণ। পরবর্তী গবেষণায় দেখা গেছে যে ডিএনএ হেলিকেজগুলো অনেক ইউক্যারিওটিক কোষে ডাইমার গঠন করে এবং ব্যাকটেরিয়াল প্রতিলিপন মেশিনারিগুলো ডিএনএ সংশ্লেষণের সময় একক অন্তর্মুখী স্থানে থাকে।[৩৩]
প্রতিলিপন কারখানাগুলো সিস্টার-ক্রোমাটিডের বিচ্ছিন্নতা সম্পাদন করে। ডিএনএ প্রতিলিপন এর পরে ক্রোমাটিড অপত্য কোষে বিতরণ করার জন্য বিচ্ছিন্নতা প্রয়োজনীয়। যেহেতু সিস্টার-ক্রোমাটিড ডিএনএ প্রতিলিপনের পরে আসঞ্জন বলয় দ্বারা একে-অপরকে ধরে রাখে, ডিএনএ প্রতিলিপনে বিচ্ছিন্ন হওয়ার একমাত্র সুযোগ আছে। প্রতিলিপন কারখানা হিসেবে প্রতিলিপন মেশিনারিকে ঠিক করা হলে ডিএনএ প্রতিলিপনের সাফল্যের হার বেড়ে যায়। যদি রেপ্লিকেশন ফর্কগুলো ক্রোমোজোমে অবাধে চলাচল করে তবে নিউক্লিয়াসের ক্যাটিনেশন ক্রমবর্ধমান হয় এবং মাইটোটিক বিভাজনকে বাধাগ্রস্ত করে।[৩৪]
সমাপ্তি সম্পাদনা
ইউক্যারিওটিক ক্রোমোজোমের একাধিক পয়েন্টে ডিএনএ প্রতিলিপন শুরু হয়, তাই রেপ্লিকেশন ফর্ক বহু পয়েন্টে মিলিত হয় এবং সমাপ্ত হয়। ইউক্যারিওটগুলোতে সরলরৈখিক ক্রোমোজোম রয়েছে বলে ডিএনএ প্রতিলিপন ক্রোমোজোমের একেবারে প্রান্তে পৌঁছাতে পারে না। এই সমস্যার কারণে ক্রোমোজোমের শেষ থেকে প্রতিটি প্রতিলিপি চক্রের মধ্যে ডিএনএ হারিয়ে যায়। টেলোমিয়ারস হলো পুনরাবৃত্ত ডিএনএর প্রান্ত নিকটবর্তী অঞ্চল এবং এটি সংক্ষিপ্তকরণের কারণে জিনের ক্ষয় রোধে সহায়তা করে। টেলোমিয়ারসের সংক্ষিপ্তকরণ দেহ কোষের একটি স্বাভাবিক প্রক্রিয়া। এটি অপত্য ডিএনএ ক্রোমোজোমের টেলোমিয়ারকে সংক্ষিপ্ত করে। ফলস্বরূপ ডিএনএ-এর ক্ষতি আরও বিভাজন রোধ করার আগে কোষগুলো কেবলমাত্র একটি নির্দিষ্ট সংখ্যক বার ভাগ হতে পারে (এটি হায়ফ্লিক সীমা হিসেবে পরিচিত)। এর মধ্যে বীজ কোষ লাইন যা পরবর্তী প্রজন্মের ডিএনএ স্থানান্তর করে, টেলোমিয়ারেজ ক্ষয় রোধ করতে টেলোমিয়ারের অঞ্চলের পুনরাবৃত্তিক ক্রমগুলো প্রসারিত করে। টেলোমিয়ারেজ ভুলভাবে দেহকোষগুলোতে সক্রিয় হয়ে উঠতে পারে, যা কখনও কখনও ক্যান্সার গঠনের দিকে পরিচালিত করে। বর্ধিত টেলোমিয়ারেজ ক্রিয়াকলাপ ক্যান্সারের অন্যতম বৈশিষ্ট্য।
সমাপ্তির জন্য ডিএনএ রেপ্লিকেশন ফর্কের অগ্রগতি অবশ্যই বন্ধ বা অবরুদ্ধ করা উচিত। একটি নির্দিষ্ট লোকাসে যখন সমাপ্তি ঘটে তখন দুটি উপাদানগুলোর মধ্যে মিথস্ক্রিয়া ঘটে: (১) ডিএনএতে একটি সমাপ্তি স্থান ক্রম এবং (২) একটি প্রোটিন যা ডিএনএর প্রতিলিপনকে শারীরিকভাবে থামানোর জন্য এই ক্রমের সাথে আবদ্ধ থাকে। বিভিন্ন ব্যাকটেরিয়া প্রজাতিগুলোতে এটির নাম দেওয়া হয় ডিএনএ রেপ্লিকেশন টার্মিনাস সাইট-বাইন্ডিং প্রোটিন, বা টার প্রোটিন।
কারণ ব্যাকটেরিয়ায় বৃত্তাকার ক্রোমোজোম থাকে, প্রতিলিপনের সমাপ্তি ঘটে যখন দুটি রেপ্লিকেশন ফর্ক মাতৃক্রোমোজোমে বিপরীত প্রান্তে একে অপরের সাথে মিলিত হয়। E. coli এই প্রক্রিয়াটি সমাপ্তি অনুক্রমগুলো ব্যবহার করে নিয়ন্ত্রণ করে যা টাস প্রোটিন দ্বারা আবদ্ধ হলে রেপ্লিকেশন ফর্ক কেবল একটি দিক দিয়ে যেতে সক্ষম হয়। ফলস্বরূপ, রেপ্লিকেশন ফর্কগুলো সর্বদা ক্রোমোজোমের সমাপ্তি অঞ্চলে পৌঁছাতে বাধা দেয়।[৩৫]
নিয়ন্ত্রণ সম্পাদনা
ইউক্যারিওটস সম্পাদনা
ইউক্যারিওটসের মধ্যে, ডিএনএ প্রতিলিপন কোষ চক্রের প্রসঙ্গ হিসেবে নিয়ন্ত্রিত হয়। কোষ এর বৃদ্ধি ও বিভাজন এর সাথে সাথে এটি কোষ চক্রের ধাপগুলোর মধ্য দিয়ে অগ্রসর হয়; ডিএনএ প্রতিলিপি এস পর্যায়ের (সংশ্লেষণ পর্ব) সময় সঞ্চালিত হয়। চক্রের মাধ্যমে ইউক্যারিওটিক কোষের অগ্রগতি কোষ চক্রের চেকপয়েন্টগুলো দ্বারা নিয়ন্ত্রিত হয় । সাইক্লিন এবং সাইক্লিন নির্ভর কাইনেজ সহ বিভিন্ন প্রোটিনের মধ্যে জটিল মিথস্ক্রিয়ার মাধ্যমে ছেকপয়েন্টগুলোর মাধ্যমে অগ্রগতি নিয়ন্ত্রণ করা হয়।[৩৬] ব্যাকটেরিয়া থেকে ভিন্ন, ইউক্যারিওটিক ডিএনএ নিউক্লিয়াসের সীমানায় প্রতিলিপি তৈরি করে।[৩৭]
G1/S চেকপয়েন্ট (বা সীমাবদ্ধতা চেকপয়েন্ট) ইউক্যারিওটিক কোষগুলো ডিএনএ প্রতিলিপন এবং পরবর্তী বিভাগের প্রক্রিয়াতে প্রবেশ করে কিনা তা নিয়ন্ত্রণ করে। এই চেকপয়েন্টের মধ্য দিয়ে অগ্রসর না হওয়া কোষগুলো G-0 পর্যায়ে থেকে যায় এবং তাদের ডিএনএ প্রতিলিপন হয় না।
G1/S চেকপয়েন্টে অতিক্রম করার সময়, ডিএনএ কে অবশ্যই প্রতিটি কোষ চক্রে একবার করে প্রতিলিপন তৈরি করতে হয়। যখন Mcm কমপ্লেক্সটি উৎস থেকে সরে যায়, প্রাক-রেপ্লিকেশন কমপ্লেক্সটি ভেঙে ফেলা হয়। যেহেতু প্রাক-রেপ্লিকেশন সাব-ইউনিটগুলো পুনরায় সক্রিয় করা না হওয়া অবধি কোন নতুন Mcm কমপ্লেক্স কোন উৎসে লোড করা যায় না, তাই প্রতিলিপনে একটি উৎস একই কোষ চক্রে দুবার ব্যবহার করা যায় না।[১৮]
প্রারম্ভিক এস পর্যায়ে S-Cdks সক্রিয়করণ তাৎক্ষণিকভাবে পুনরুদ্ধার প্রতিরোধ করে প্রাক-রেপ্লিকেশন কমপ্লেক্স এর উপাদানগুলোর ধ্বংস বা বাধা দান করে। S এবং M-Cdks এস-ফেজ শেষ হওয়ার পরেও প্রাক-রেপ্লিকেশন কমপ্লেক্স একত্রিত হওয়াকে অবরুদ্ধ করে রাখে, এটি নিশ্চিত করে যে মাইটোসিস এ সমস্ত Cdk ক্রিয়াকলাপ হ্রাস না করা পর্যন্ত সমাবেশ আবার ঘটতে পারে না।[১৮]
মুকুলোদগম করে এমন ইস্টে, প্রাক-রেপ্লিকেশন কমপ্লেক্স উপাদানগুলোর সিডিকে-নির্ভর ফসফোরাইলেশনের কারণে সমাবেশের বাধা ঘটে। এস পর্বের শুরুতে, Cdk1 দ্বারা Cdc6 এর ফসফোরাইলেশনের ফলে SCF ইউবুইকিটিন প্রোটিন লাইগেজের সাথে Cdc6 আবদ্ধ হয়, যা Cdc6 এর প্রোটিওলাইটিক ভাঙ্গন ঘটায়। এস পর্বে Mcm প্রোটিনগুলোর Cdk নির্ভর ফসফোরাইলেশন Cdk1 এর সাথে নিউক্লিয়াসের বাইরে তাদের বের করে, একক কোষ চক্রের সময় উৎসে নতুন Mcm কমপ্লেক্সগুলো লোড করা রোধ করে। উৎসের রেপ্লিকেশন কমপ্লেক্সের Cdk ফসফোরাইলেশন প্রাক-রেপ্লিকেশন কমপ্লেক্সের সমাবেশকে বাধা দেয়। এই তিনটি পদ্ধতির যেকোনটির পৃথক উপস্থিতি প্রাক-রেপ্লিকেশন কমপ্লেক্সের সমাবেশকে বাধা দেওয়ার জন্য যথেষ্ট। যাইহোক, একই কোষে তিনটি প্রোটিনের মিউটেশন একটি কোষ চক্রের মধ্যে প্রতিলিপন এর অনেক উৎস পুনরুদ্ধারকে ট্রিগার করে।[১৮][৩৮]
প্রাণী কোষগুলোতে, প্রোটিন জেমিনিন প্রাক-রেপ্লিকেশন কমপ্লেক্সের সমাবেশের মূল প্রতিবন্ধক। জেমিনিন Cdt1 কে বেঁধে রাখে, এটিকে উৎস স্বীকৃতি কমপ্লেক্সের সাথে আবদ্ধ হওয়া থেকে রোধ করে। জি-১ এ, APC দ্বারা জেমিনের মাত্রা কম রাখা হয়, যা জেমিনিনকে অবক্ষয়ের জন্য লক্ষ্যবস্তু করে তোলে। জেমিনিন ধ্বংস হয়ে গেলে, Cdt1 প্রকাশ পায়, এটি প্রাক-রেপ্লিকেশন কমপ্লেক্সের সমাবেশ গঠনে কাজ করে। জি-১ এর শেষে, APC নিষ্ক্রিয় হয়, জেমিনিনকে জমা করে এবং Cdt1 এর সাথে যুক্ত করে।[১৮]
ক্লোরোপ্লাস্ট এবং মাইটোকন্ড্রিয়াল জিনোমের প্রতিলিপন ডি-লুপ প্রতিলিপন প্রক্রিয়াটির মাধ্যমে কোষ চক্রের স্বাধীনভাবে ঘটে।
রেপ্লিকেশন ফোকাস সম্পাদনা
কশেরুকা কোষে, প্রতিলিপন সাইটগুলো রেপ্লিকেশন ফোকি[৩৪] নামক পজিশনে মনোনিবেশ করে। প্রতিলিপি সাইটগুলো অপত্য স্ট্র্যান্ড এবং প্রতিলিপন এনজাইমগুলো প্রতিরোধক এবং GFP-ট্যাগযুক্ত রেপ্লিকেশন ফ্যাক্টরগুলো পর্যবেক্ষণ করে শনাক্ত করা যেতে পারে। এই পদ্ধতিগুলোর মাধ্যমে এটি পাওয়া যায় যে কোষ বিভাজনের এস পর্যায়ে বিভিন্ন আকারের এবং অবস্থানের রেপ্লিকেশন ফোকি প্রদর্শিত হয় এবং নিউক্লিয়াস প্রতি তাদের সংখ্যা জিনোমিক রেপ্লিকেশন ফর্ক সংখ্যার তুলনায় অনেক কম।
পি হিউন ও তার সহযোগীরা[৩৪] (২০০১) মুকুলোদগম কারী ইস্ট কোষগুলোতে GFP-ট্যাগযুক্ত রেপ্লিকেশন ফোকি শনাক্ত করেছেন এবং প্রকাশ করেছেন যে প্রতিলিপি উৎসটি জি-১ এবং এস পর্যায়ে অবিচ্ছিন্ন ভাবে সরানো হয় এবং এস পর্যায়ে গতিশীলতা উল্লেখযোগ্যভাবে হ্রাস পায়।[৩৪] প্রচলিত ধারণা অনুযায়ী, রেপ্লিকেশন সাইটগুলো ক্রোমোজোমের স্থানিক কাঠামোর ক্ষেত্রে পারমাণবিক ম্যাট্রিক্স বা ল্যামিন দ্বারা স্থির করা হয়। হিউনের ফলাফল প্রচলিত ধারণাগুলোকে অস্বীকার করেছে, মুকুলোদগম কারী ইয়েস্টগুলোতে ল্যামিন নেই কিন্তু প্রতিলিপন উৎসের আত্ম-জমায়েত হয় এবং রেপ্লিকেশন ফোকি তৈরি হয়।
স্থানিক ও সাময়িকভাবে নিয়ন্ত্রিত প্রতিলিপন উৎসগুলো চালিয়ে, রেপ্লিকেশন ফোকি গঠন নিয়ন্ত্রিত হয়। ডিএ জ্যাকসন ও তার সহযোগীরা (১৯৯৮) প্রকাশ করেছেন যে প্রতিবেশী উৎস স্তন্যপায়ী কোষগুলোতে একই সাথে বহিষ্কার হয়।[৩৪] প্রতিলিপন সাইটগুলোর স্থানিক পাশাপাশি অবস্থান রেপ্লিকেশন ফর্কগুলোর ক্লাস্টারিং নিয়ে আসে। ক্লাস্টারিং স্থগিত রেপ্লিকেশন ফর্কগুলো উদ্ধার করে এবং রেপ্লিকেশন ফর্কগুলোর স্বাভাবিক অগ্রগতি ফিরিয়ে আনে। রেপ্লিকেশন ফর্কগুলোর অগ্রগতি অনেকগুলো কারণ দ্বারা প্রতিহত হয়; প্রোটিনের সাথে বা ডিএনএর সাথে দৃঢ়ভাবে আবদ্ধ কমপ্লেক্সগুলোর সাথে সংঘর্ষ, dNTPs-র অভাব, টেমপ্লেট ডিএনএ-র নিকগুলো ইত্যাদি। যদি স্টল রেপ্লিকেশন ফর্ক এবং স্ট্রিট প্রতিলিপি থেকে অবশিষ্ট ক্রমগুলো প্রতিলিপিত না করা হয় তবে অপত্য স্ট্র্যান্ডগুলো অপ্রতিলিপিত সাইটগুলো পায়। এক মাতৃ স্ট্র্যান্ডের অপ্রতিলিপিত সাইটগুলো অন্য স্ট্র্যান্ডকে একত্রে ধারণ করে তবে অপত্য স্ট্র্যান্ডকে নয়। সুতরাং, ফলস্বরূপ সিস্টার-ক্রোমাটিডগুলো একে অপরের থেকে পৃথক হতে পারে না এবং দুটি অপত্য কোষে বিভক্ত হতে পারে না। প্রতিবেশী উৎসে বহিষ্কার এবং একটি উৎস থেকে স্থবির ফর্ক প্রতিলিপিত হয়ে গেলে, অন্য উৎস থেকে ফর্ক বিপরীত দিকে পৌঁছায় এবং অপ্রতিলিপিত সাইটগুলো প্রতিলিপন করে। উদ্ধারের অন্যান্য প্রক্রিয়া হিসেবে প্রয়োগ এর মধ্যে রয়েছে সুপ্ত প্রতিলিপন উৎস যা সাধারণ ডিএনএ প্রতিলিপন অতিরিক্ত উৎসগুলো বহিষ্কার করে দেয় না।
ব্যাকটেরিয়া সম্পাদনা
বেশিরভাগ ব্যাকটেরিয়া একটি ভাল সংজ্ঞায়িত কোষ চক্রের মধ্যে দিয়ে যায় না বরং পরিবর্তে তাদের ডিএনএ অনবরত অনুলিপিত করে; দ্রুত বর্ধনের সময়, এটি একই সময়ে প্রতিলিপন এর একাধিক রাউন্ডের ঘটাতে সাহায্য করে।[৩৯] E. coli তে, শ্রেষ্ঠ বৈশিষ্ট্যযুক্ত ব্যাকটেরিয়া, ডিএনএ রেপ্লিকেশন বিভিন্ন প্রক্রিয়ার মাধ্যমে নিয়ন্ত্রিত হয়, যেমন: হেমি-মিথাইলেশন এবং উৎপত্তি ক্রম স্বতন্ত্র রাখা, অনুপাত এডিনোসিন ট্রাইফসফেট (ATP) থেকে এডিনোসিন ডাইফসফেট (ADP), এবং প্রোটিন DnaA স্তর দ্বারা। এগুলো সমস্ত সূত্রকের সূচনাতে প্রবর্তক প্রোটিনের বাঁধাই নিয়ন্ত্রণ করে।
কারণ E. coli GATC ডিএনএ সিকোয়েন্সকে মিথাইলেশন করে, হেমি-মিথাইলেটেড সিকোয়েন্স মধ্যে ডিএনএ সংশ্লেষণ এর ফলাফল নেই। এই হেমি-মিথাইলেটেড ডিএনএ প্রোটিন SeqA দ্বারা শনাক্ত করা হয়, যা মূল ক্রমকে আবদ্ধ করে এবং পৃথক করে; তদ্ব্যতীত, DnaA (প্রতিলিপন সূচনা করার জন্য প্রয়োজনীয়) হেমিমেথিলিটেড ডিএনএকে কম ভালভাবে আবদ্ধ করে। ফলস্বরূপ, নতুন প্রতিলিপিযুক্ত উৎসগুলো তাৎক্ষণিক ডিএনএর অনুলিপন এর অন্য রাউন্ড শুরু করতে বাধা দেয়।[৪০]
ATP তৈরি হয় যখন কোষটি একটি সমৃদ্ধ মাধ্যমে থাকে, যা একটি নির্দিষ্ট আকারে পৌঁছে যাওয়ার পরে ডিএনএ প্রতিলিপনে ট্রিগার করে। ATP DnaA সাথে যুক্ত হতে ADP এর সাথে প্রতিযোগিতা করে এবং DnaA-ATP কমপ্লেক্স প্রতিলিপন শুরু করতে সক্ষম হয়। ডিএনএর প্রতিলিপনের জন্য একটি নির্দিষ্ট সংখ্যক DnaA প্রোটিনও প্রয়োজন - প্রতিবার উৎসটি অনুলিপি করা হলে, DnaA এর জন্য বাইন্ডিং সাইটগুলোর সংখ্যা দ্বিগুণ হয়ে যায়, যাতে আরও ডিএনএর সংশ্লেষণের প্রয়োজন হয় যাতে আরেকটি প্রতিলিপন সূচনা করতে।
E. coli এর মতো দ্রুত বর্ধমান ব্যাকটেরিয়াতে ক্রোমোজোম প্রতিলিপন কোষ বিভাজনের চেয়ে বেশি সময় নেয়। ব্যাকটেরিয়াগুলো এর পরবর্তী রাউন্ড শেষ হওয়ার আগে প্রতিলিপন এর নতুন রাউন্ড শুরু করে এটি সমাধান করে।[৪১] প্রতিলিপনের নতুন রাউন্ডটি কোষের ক্রোমোজোম গঠন করবে যা থেকে পরবর্তীতে কোষ বিভাজনের মাধ্যমে দুই প্রজন্ম জন্মগ্রহণ করে। এই প্রক্রিয়াটি ওভারল্যাপিং প্রতিলিপন চক্র তৈরি করে।
ডিএনএ প্রতিলিপনের সমস্যা সম্পাদনা
রেপ্লিকেশন স্ট্রেস এর অনেকগুলো কারণ বা ঘটনা রয়েছে, এর মধ্যে আছে[৪২] -
- রাইবো-নিউক্লিওটাইডগুলোর ভুল সংস্থান
- অস্বাভাবিক ডিএনএ কাঠামো
- প্রতিলিপন এবং ট্রানস্ক্রিপশন এর মধ্যে দ্বন্দ্ব
- অপরিহার্য প্রতিলিপন ফ্যাক্টরগুলোর অপর্যাপ্ততা
- সাধারণ ভঙ্গুর সাইটগুলো
- ওভার-এক্সপ্রেশন অথবা অঙ্কোজিনের মৌলিক অ্যাক্টিভেশন
- ক্রোমাটিন এর অপ্রাপ্যতা
পলিমারেজ চেইন বিক্রিয়া সম্পাদনা
গবেষকরা সাধারণত গবেষণাগারের মধ্যে পলিমারেজ চেইন বিক্রিয়া (PCR) ব্যবহার করে ডিএনএ প্রতিলিপিকরণ সম্পন্ন করেন। পিসিআর একজোড়া প্রাইমার ব্যবহার করে টেমপ্লেট ডিএনএর লক্ষ্য অঞ্চল বিস্তার লাভ করে এবং তারপরে থার্মোস্টেবল ডিএনএ পলিমারেজ ব্যবহার করে এই প্রাইমারের কাছ থেকে প্রতিটি দিকে অংশীদার স্ট্র্যান্ডকে পলিমারাইজ করে। একাধিক চক্রের মাধ্যমে এই প্রক্রিয়াটির পুনরাবৃত্তি লক্ষ্যযুক্ত ডিএনএ অঞ্চলকে প্রশস্ত করে। প্রতিটি চক্রের শুরুতে, টেমপ্লেট এবং প্রাইমারের মিশ্রণটি উত্তপ্ত হয়, নতুন সংশ্লেষিত অণু এবং টেমপ্লেটকে পৃথক করে। তারপরে, মিশ্রণটি শীতল হওয়ার সাথে সাথে উভয়ই নতুন প্রাইমারের অ্যানেলিং এর জন্য টেমপ্লেট হয়ে যায় এবং পলিমারেজগুলো এগুলো থেকে প্রসারিত হয়। ফলস্বরূপ, লক্ষ্য অঞ্চলের অনুলিপিগুলোর সংখ্যা প্রতিটি রাউন্ড শেষে দ্বিগুণ হয়, তাৎপর্যপূর্ণভাবে বৃদ্ধি পায়।[৪৩]
আরও দেখুন সম্পাদনা
তথ্যসূত্র সম্পাদনা
- ↑ "What is DNA Replication and Its Steps? » Micro B Life"। Micro B Life (ইংরেজি ভাষায়)। ২০২০-০৫-২৫। সংগ্রহের তারিখ ২০২১-০৩-২৪।[স্থায়ীভাবে অকার্যকর সংযোগ]
- ↑ "GENETICS / DNA REPLICATION (BASIC) - Pathwayz"। www.pathwayz.org। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ "double helix | Learn Science at Scitable"। www.nature.com। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ Pray, LA। "Semi-Conservative DNA Replication; Meselson and Stahl"।
- ↑ "Biochemistry [electronic resource] : Berg, Jeremy M. (Jeremy Mark), 1958- : Free Download, Borrow, and Streaming : Internet Archive"। web.archive.org। ২০২০-০৩-২৬। Archived from the original on ২০২০-০৩-২৬। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ ক খ Lodish, Harvey; Berk, Arnold; Zipursky, S. Lawrence; Matsudaira, Paul; Baltimore, David; Darnell, James (২০০০)। "DNA Replication, Repair, and Recombination"। Molecular Cell Biology. 4th edition (ইংরেজি ভাষায়)।
- ↑ ক খ "Biochemistry [electronic resource] : Berg, Jeremy M. (Jeremy Mark), 1958- : Free Download, Borrow, and Streaming : Internet Archive"। web.archive.org। ২০২০-০৩-২৬। Archived from the original on ২০২০-০৩-২৬। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ "What is a genome?"। yourgenome (ইংরেজি ভাষায়)। ২০২২-০৯-০১ তারিখে মূল থেকে আর্কাইভ করা। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ "DNA function & structure (with diagram) (article)"। Khan Academy (ইংরেজি ভাষায়)। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ Alberts B; ও অন্যান্য (২০০২)। Molecular Biology of the Cell (4th ed.)। Garland Science। পৃষ্ঠা ২৩৮–২৪০। আইএসবিএন 0-8153-3218-1।
- ↑ Berg, Jeremy M.; Tymoczko, John L.; Stryer, Lubert (২০০২)। "DNA Polymerases Require a Template and a Primer"। Biochemistry. 5th edition (ইংরেজি ভাষায়)।
- ↑ ক খ McCulloch, Scott D.; Kunkel, Thomas A. (২০০৮)। "The fidelity of DNA synthesis by eukaryotic replicative and translesion synthesis polymerases"। Cell Research (ইংরেজি ভাষায়)। 18 (1): 148–161। আইএসএসএন 1748-7838। ডিওআই:10.1038/cr.2008.4। পিএমআইডি 18166979। পিএমসি 3639319 ।
- ↑ McCarthy, David; Minner, Charles; Bernstein, Harris; Bernstein, Carol (১৯৭৬-১০-০৫)। "DNA elongation rates and growing point distributions of wild-type phage T4 and a DNA-delay amber mutant"। Journal of Molecular Biology (ইংরেজি ভাষায়)। 106 (4): 963–981। আইএসএসএন 0022-2836। ডিওআই:10.1016/0022-2836(76)90346-6।
- ↑ Drake, JW (১৯৭০)। The Molecular Basis of Mutation। San Francisco: Holden-Day। আইএসবিএন 978-0816224500।
- ↑ Alberts, Bruce; Johnson, Alexander; Lewis, Julian; Raff, Martin; Roberts, Keith; Walter, Peter (২০০২)। "DNA Replication Mechanisms"। Molecular Biology of the Cell. 4th edition (ইংরেজি ভাষায়)।
- ↑ Weigel, Christoph; Schmidt, Andrea; Rückert, Beate; Lurz, Rudi; Messer, Walter (১৯৯৭-১১-০১)। "DnaA protein binding to individual DnaA boxes in the Escherichia coli replication origin, oriC"। The EMBO Journal। 16 (21): 6574–6583। আইএসএসএন 0261-4189। ডিওআই:10.1093/emboj/16.21.6574। পিএমআইডি 9351837। পিএমসি 1170261 ।[স্থায়ীভাবে অকার্যকর সংযোগ]
- ↑ Lodish, Harvey F. (২০০০)। Molecular cell biology। Internet Archive। New York : W.H. Freeman। আইএসবিএন 978-0-7167-3136-8।
- ↑ ক খ গ ঘ ঙ চ ছ জ ঝ Morgan, David Owen (২০০৭)। The cell cycle: principles of control (English ভাষায়)। London; Sunderland, MA: New Science Press ; Sinauer Associates। আইএসবিএন 978-0-19-920610-0। ওসিএলসি 70173205।
- ↑ Donaldson, Anne D; Raghuraman, M.K; Friedman, Katherine L; Cross, Frederick R; Brewer, Bonita J; Fangman, Walton L (১৯৯৮)। "CLB5-Dependent Activation of Late Replication Origins in S. cerevisiae"। Molecular Cell। 2 (2): 173–182। আইএসএসএন 1097-2765। ডিওআই:10.1016/s1097-2765(00)80127-6।
- ↑ Aravind, L.; Leipe, Detlef D.; Koonin, Eugene V. (১৯৯৮-০৯-০১)। "Toprim—a conserved catalytic domain in type IA and II topoisomerases, DnaG-type primases, OLD family nucleases and RecR proteins"। Nucleic Acids Research। 26 (18): 4205–4213। আইএসএসএন 0305-1048। ডিওআই:10.1093/nar/26.18.4205। পিএমআইডি 9722641। পিএমসি 147817 ।
- ↑ Frick, David N.; Richardson, Charles C. (২০০১-০৬-০১)। "DNA Primases"। Annual Review of Biochemistry। 70 (1): 39–80। আইএসএসএন 0066-4154। ডিওআই:10.1146/annurev.biochem.70.1.39। ২০২১-০৭-২৮ তারিখে মূল থেকে আর্কাইভ করা। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ Barry, Elizabeth R.; Bell, Stephen D. (২০০৬-১২-০১)। "DNA Replication in the Archaea"। Microbiology and Molecular Biology Reviews (ইংরেজি ভাষায়)। 70 (4): 876–887। আইএসএসএন 1092-2172। ডিওআই:10.1128/MMBR.00029-06। পিএমআইডি 17158702। পিএমসি 1698513 ।
- ↑ Stillman, Bruce (২০১৫)। "Reconsidering DNA Polymerases at the Replication Fork in Eukaryotes"। Molecular Cell। 59 (2): 139–141। আইএসএসএন 1097-2765। ডিওআই:10.1016/j.molcel.2015.07.004। পিএমআইডি 26186286। পিএমসি 4636199 ।
- ↑ Rossi, Marie (২০০৮)। "Distinguishing the pathways of primer removal during Eukaryotic Okazaki fragment maturation"।
- ↑ Huberman, Joel A.; Riggs, Arthur D. (১৯৬৮-০৩-১৪)। "On the mechanism of DNA replication in mammalian chromosomes"। Journal of Molecular Biology (ইংরেজি ভাষায়)। 32 (2): 327–341। আইএসএসএন 0022-2836। ডিওআই:10.1016/0022-2836(68)90013-2।
- ↑ Gao, Yang; Cui, Yanxiang; Fox, Tara; Lin, Shiqiang; Wang, Huaibin; Val, Natalia de; Zhou, Z. Hong; Yang, Wei (২০১৯-০২-২২)। "Structures and operating principles of the replisome"। Science (ইংরেজি ভাষায়)। 363 (6429)। আইএসএসএন 0036-8075। ডিওআই:10.1126/science.aav7003। পিএমআইডি 30679383। পিএমসি 6681829 ।
- ↑ Wilson, John; Hunt, Tim (২০০২)। Molecular biology of the cell : a problems approach। Internet Archive। New York : Garland Science। আইএসবিএন 978-0-8153-3577-1।
- ↑ Reece, Richard J.; Maxwell, Anthony (১৯৯১-০১-০১)। "DNA Gyrase: Structure and Function"। Critical Reviews in Biochemistry and Molecular Biology। 26 (3-4): 335–375। আইএসএসএন 1040-9238। ডিওআই:10.3109/10409239109114072। পিএমআইডি 1657531।
- ↑ Alberts, Bruce; Johnson, Alexander; Lewis, Julian; Raff, Martin; Roberts, Keith; Walter, Peter (২০০২)। "DNA Replication Mechanisms"। Molecular Biology of the Cell. 4th edition (ইংরেজি ভাষায়)।
- ↑ Ransom, Monica; Dennehey, Briana K.; Tyler, Jessica K. (২০১০)। "Chaperoning Histones during DNA Replication and Repair"। Cell। 140 (2): 183–195। আইএসএসএন 0092-8674। ডিওআই:10.1016/j.cell.2010.01.004। পিএমআইডি 20141833। পিএমসি 3433953 ।
- ↑ Griffiths, AJ; Wessler, SR; Lewontin, RC; Carroll, SB (২০০৮)। "Chapter 7: DNA: Structure and Replication"। Introduction to Genetic Analysis। W. H. Freeman and Company। পৃষ্ঠা ২৮৩–২৯০। আইএসবিএন 978-0-7167-6887-6।
- ↑ "Will the Hayflick limit keep us from living forever?"। HowStuffWorks (ইংরেজি ভাষায়)। ২০০৯-০৫-১১। সংগ্রহের তারিখ ২০২১-০৩-২৪।
- ↑ ক খ James D., Watson; ও অন্যান্য (২০০৮)। Molecular Biology of the gene। Pearson Education। পৃষ্ঠা ২৩৭।
- ↑ ক খ গ ঘ ঙ চ Peter, Meister; Angela, Taddei1; Susan M., Gasser (২০০৬)। "In and out of the Replication Factory"। Cell। পৃষ্ঠা ১২৩৩–১২৩৫।
- ↑ Brown, Terence A. (২০০২)। Genome Replication (ইংরেজি ভাষায়)। Wiley-Liss।
- ↑ Alberts, Bruce; Johnson, Alexander; Lewis, Julian; Raff, Martin; Roberts, Keith; Walter, Peter (২০০২)। "Intracellular Control of Cell-Cycle Events"। Molecular Biology of the Cell. 4th edition (ইংরেজি ভাষায়)।
- ↑ Brown, Terence A. (২০০২)। Genome Replication (ইংরেজি ভাষায়)। Wiley-Liss।
- ↑ Nguyen, Van Q.; Co, Carl; Li, Joachim J. (২০০১)। "Cyclin-dependent kinases prevent DNA re-replication through multiple mechanisms"। Nature (ইংরেজি ভাষায়)। 411 (6841): 1068–1073। আইএসএসএন 1476-4687। ডিওআই:10.1038/35082600।
- ↑ Tobiason, Deborah M.; Seifert, H. Steven (২০০৬-০৫-৩০)। "The Obligate Human Pathogen, Neisseria gonorrhoeae, Is Polyploid"। PLOS Biology (ইংরেজি ভাষায়)। 4 (6): e185। আইএসএসএন 1545-7885। ডিওআই:10.1371/journal.pbio.0040185। পিএমআইডি 16719561। পিএমসি 1470461 ।
- ↑ Slater, Steven; Wold, Sture; Lu, Min; Boye, Erik; Skarstad, Kirsten; Kleckner, Nancy (১৯৯৫)। "E. coli SeqA protein binds oriC in two different methyl-modulated reactions appropriate to its roles in DNA replication initiation and origin sequestration"। Cell। 82 (6): 927–936। আইএসএসএন 0092-8674। ডিওআই:10.1016/0092-8674(95)90272-4।
- ↑ Cooper, Stephen; Helmstetter, Charles E. (১৯৬৮-০২-১৪)। "Chromosome replication and the division cycle of Escherichia coli Br"। Journal of Molecular Biology (ইংরেজি ভাষায়)। 31 (3): 519–540। আইএসএসএন 0022-2836। ডিওআই:10.1016/0022-2836(68)90425-7।
- ↑ Zeman, Michelle K.; Cimprich, Karlene A. (২০১৪)। "Causes and consequences of replication stress"। Nature Cell Biology (ইংরেজি ভাষায়)। 16 (1): 2–9। আইএসএসএন 1476-4679। ডিওআই:10.1038/ncb2897। পিএমআইডি 24366029। পিএমসি 4354890 ।
- ↑ Saiki, R. K.; Gelfand, D. H.; Stoffel, S.; Scharf, S. J.; Higuchi, R.; Horn, G. T.; Mullis, K. B.; Erlich, H. A. (১৯৮৮-০১-২৯)। "Primer-directed enzymatic amplification of DNA with a thermostable DNA polymerase"। Science (ইংরেজি ভাষায়)। 239 (4839): 487–491। আইএসএসএন 0036-8075। ডিওআই:10.1126/science.239.4839.487। পিএমআইডি 2448875।